L'analisi omica integrativa svela i percorsi correlati all'infiammazione microvascolare nelle biopsie di allotrapianto renale
Mar 24, 2022
Nel trapianto di organi solidi, i microRNA (miRNA) sono emersi come attori chiave nella regolazione della funzione delle cellule di allotrapianto in risposta al danno. Per ottenere informazioni sul ruolo dei miRNA nel rigetto mediato da anticorpi, un fenotipo di rigetto definito istologicamente dall'infiammazione microvascolare,rene le biopsie dell'allotrapianto sono state sottoposte a profilazione di miRNA ma anche di RNA messaggero (mRNA). Utilizzando un processo di selezione multistep unico specifico per lo studio BIOMARGIN (coorte di scoperta, N=86; coorte di selezione, N=99; coorte di convalida, N=298), sono stati identificati in modo coerente sei miRNA espressi in modo differenziale: miR-139-5p (down) e miR-142-3p/150-5p/155-5p/{ {7}}p/223-3p (su). Il loro livello di espressione è gradualmente correlato all'intensità dell'infiammazione microvascolare. La specificità cellulare dei geni bersaglio dei miRNA è stata studiata integrando i loro bersagli mRNA in vivo con il sequenziamento dell'RNA unicellulare da una coorte di biopsia di allotrapianto indipendente. L'espressione di miR-139-5p derivata dall'endotelio era correlata negativamente con l'espressione dei geni correlati a MHC. Al contrario, la sovraespressione di miR-222-3p derivata dall'epitelio era fortemente associata all'omeostasi degli elettroliti renali degradata e alle vie immunitarie represse. Nelle cellule immunitarie, miR-150-5p regolava l'attivazione di NF-kB nei linfociti T mentre miR-155-5p regolava lo splicing dell'mRNA nelle cellule presentanti l'antigene. Complessivamente, l'omica integrata ci ha permesso di svelare nuovi percorsi coinvolti nell'infiammazione microvascolare e suggerisce che le modificazioni del metabolismo nelle cellule epiteliali tubulari si verificano come conseguenza del rigetto mediato da anticorpi, oltre il vicino compartimento endoteliale.
Parole chiave:trapianto di rene, microRNA, multi-omica, infiammazione microvascolare, rigetto mediato da anticorpi

CISTANCHE MIGLIORA LA MALATTIA RENALE/RENALE
INTRODUZIONEIntrapianto di rene(KT), il danno alloimmune è solitamente dicotomizzato in due tipi di rigetto dell'allotrapianto in base alla distribuzione spaziale dell'infiltrazione immunitaria e alle informazioni sulla presenza o assenza di anticorpi anti-HLA specifici del donatore. La diagnosi si basa sulla biopsia dell'allotrapianto con la classificazione delle lesioni istologiche secondo la classificazione del Banff International Consensus(1). La tubulite (lesione "t") e l'infiammazione interstiziale (lesione "I") sono caratteristiche istologiche tipiche del rigetto mediato dai linfociti T (TCMR) e sono correlate alla citotossicità diretta al compartimento tubulo-interstiziale. Il rigetto mediato da anticorpi (ABMR) è più spesso associato alla circolazione di anticorpi anti-HLA con infiammazione mirata al compartimento microvascolare. Le lesioni istologiche ABMR attive comprendono la presenza di cellule mononucleate nei capillari glomerulari (lesione "g") e nei capillari peritubulari (lesione "ptc"), denominate congiuntamente "infiammazione microvascolare" (MVI). Nell'ABMR cronica attiva, le lesioni tissutali croniche come la glomerulopatia da trapianto o la fibrosi intimale arteriosa si sommano a queste lesioni acute(1). Utilizzando gli attuali agenti immunosoppressori mirati ai linfociti T, si ritiene che la TCMR abbia un impatto prognostico limitato, mentre l'ABMR è una delle principali cause di fallimento del trapianto, che si riferisce alla mancanza di approcci terapeutici efficaci (2).
Al fine di trovare terapie migliori per MVI e ABMR, è necessaria una migliore comprensione dei meccanismi biologici alla base di questi processi di lesione. Le tecnologie omiche ad alto rendimento sembrano adatte allo scopo poiché consentono lo screening esatto e simultaneo di migliaia di geni, proteine e metaboliti(3). Interrogatorio del trascrittoma intero direnele biopsie di allotrapianto hanno dimostrato profondi cambiamenti nell'espressione genica dell'mRNA nelle cellule residenti danneggiate o nelle popolazioni cellulari infiltranti durante l'ABMR(4). Nel frattempo, i microRNA (miRNA) sono emersi come attori chiave nel metabolismo cellulare, regolando l'RNA messaggero (mRNA) a livello post-trascrizionale. In effetti, i miRNA hanno rivoluzionato la nostra comprensione della messa a punto dei processi fisiologici del corpo coinvolti nella proliferazione, apoptosi, differenziazione e sviluppo(5). Non sorprende che l'espressione disregolata di miRNA porti allo sviluppo di molte patologie tra cuimalattia renale(6). Poiché i profili di espressione dei miRNA differiscono tra stati malati e sani, molti studi hanno analizzato i miRNA da soli o in combinazione con altri marcatori più tradizionali, non solo per diagnosticare la malattia e prognosticare la progressione della malattia, ma anche per progettare potenziali applicazioni terapeutiche (7).
Nel contesto del trapianto di organi solidi, i miRNA possono essere coinvolti nel rigetto attraverso il loro ruolo nella regolazione della funzione delle cellule immunitarie e nella risposta al danno delle cellule residenti nell'allotrapianto (6,8). Diversi studi hanno studiato i miRNA di allotrapianto come biomarcatori e/o effettori nelle impostazioni di TCMR (8,9), ma nessuno si è finora concentrato su MVI e ABMR. In questo studio, abbiamo mirato a integrare diversi livelli omici darenebiopsie di allotrapianto, per ottenere informazioni sul ruolo dei miRNA in questo fenotipo di rigetto deleterio.
MATERIALI E METODI Progetto di studioQuesto studio fa parte di BIOMarkers ofRenaleProgramma di ricerca Graft INjuries (BIOMARGIN, https://cordis.europa. eu/project/id/305499, ClinicalTrials.goy, numero NCT02832661), guidato da un consorzio di ricerca europeo alla ricerca di biomarcatori di lesioni immunitarie da allotrapianto intrapianto renaledestinatari, con valore diagnostico e/o prognostico. BIOMARGIN è uno studio multicentrico, prospettico, multifase, eseguito a quattrotrapianto renalecentri in Europa (Necker Hospital, Parigi, Francia; Ospedali universitari, Leuven, Belgio; Hannover Medical School, Hannover, Germania; e University Hospital, Limoges, Francia). I campioni sono stati raccolti in modo prospettico al momento dello screening e delle biopsie di indicazione tra aprile 2013 e giugno 2015 (Figura IA). Tutti i trapianti sono stati eseguiti con corrispondenze incrociate di citotossicità dipendente dal complemento negativo. In questi quattro centri clinici, oltre alle biopsie di indicazione, sono state eseguite biopsie di protocollo a 3,12 e talvolta a 24 mesi dal trapianto, secondo la pratica del centro locale. Il comitato di revisione istituzionale di ciascun sito ha approvato lo studio e tutti i pazienti hanno fornito il consenso informato scritto.
Coorti di studioLo studio è stato suddiviso in tre fasi (Figura 1A). Nella prima fase di scoperta caso-controllo, sono stati utilizzati N=88 campioni di biopsia per l'analisi dell'espressione di miRNA globale (N=754 miRNA, esclusi i potenziali miRNA normalizzanti) . Abbiamo selezionato i campioni in base alla disponibilità e ai criteri istologici (esclusi i casi con diagnosi di glomerulonefrite o nefropatia associata a poliomavirus e casi con diagnosi poco chiara). Sulla base delle letture della biopsia locale, è stata effettuata una prima selezione, ulteriormente affinata attraverso la lettura centrale da parte di un gruppo di patologi, indipendenti dal centro originario. L'analisi statistica (vedi selezione miRNA) è stata utilizzata per selezionare l'elenco esteso di miRNA, espressi in modo più differenziato tra i fenotipi istologici, che sono stati successivamente quantificati nella 2a fase.
Un disegno di studio caso-controllo simile è stato utilizzato per la seconda fase (selezione), in cui è stata eseguita l'analisi mirata dell'espressione di miRNA (N=143) su campioni bioptici N=99. La stessa pipeline statistica è stata applicata per selezionare un elenco ancora più ristretto di miRNA, da quantificare successivamente nella 3a fase. Infine, nella terza coorte (di convalida), tutti i campioni raccolti prospetticamente e consecutivamente secondo il protocollo BIOMARGIN tra il 24 giugno 2014 e il 2 luglio 2015, e con adeguatirenela qualità della biopsia dell'allotrapianto, sono stati valutati per i 38 miRNA selezionati come risultato della seconda fase di selezione. In questa coorte di contesti di vita reale, non è stata effettuata alcuna selezione in base all'istologia, ai dati demografici, al tempo o a qualsiasi fattore diverso dalla disponibilità del campione e dai criteri di controllo della qualità (adeguatezza della biopsia e resa dell'RNA).


Selezione del miRNAUna solida pipeline statistica è stata sviluppata specificamente per lo studio BIOMARGIN in R(R Core Team(10), versione 1.0.44), come estensione del pacchetto R biosignal(1l). In breve, nella fase di scoperta, abbiamo condotto una strategia di selezione delle caratteristiche che include approcci univariati e multivariati. Per la selezione univariata, abbiamo utilizzato un test non parametrico (test di Wilcoxon-Mann-Whitney) e un test parametrico (test t di Student) e una coorte Discovery (BIOS-03-0023, BIOS{9}}). I punteggi di previsione di ciascuna trascrizione di miRNA in ciascun modello multivariato sono stati integrati per produrre un "punteggio multivariato". Combinando i risultati di queste analisi univariate e multivariate, siamo stati in grado di classificare e selezionare un sottoinsieme di candidati miRNA da inserire nell'elenco esteso da quantificare durante la fase successiva.Per questa analisi post-hoc incentrata sui percorsi VMI, l'espressione mediana normalizzata di ciascun miRNA è stata confrontata tra casi e controlli utilizzando il test di Wilcoxon in tutte e tre le coorti. Abbiamo controllato per più test utilizzando il metodo Benjamini & Hochberg false discovery rate (FDR).
Valutazione clinicopatologicaI punteggi delle singole lesioni istologiche sono stati valutati semiquantitativamente secondo i criteri Banff 2019(16). Il termine "infiammazione microvascolare" (MVI) è stato utilizzato per riferirsi a qualsiasi grado di combinazione di glomerulite (g) e/o capillare peritubulare (ptc). Tutti i casi ABMR soddisfacevano i primi 2 criteri della classificazione Banf 2015 o Banff 2017 (istologica evidenza di danno tissutale acuto e evidenza di interazione anticorpale attuale/recente con l'endotelio vascolare), ma non tutti hanno soddisfatto il terzo criterio [evidenza sierologica di anticorpi donatori specifici (DSA) e/o colorazione CAd]. I DSA dopo il trapianto sono stati determinati in base alla pratica del centro locale, con positività DSA definita come anticorpi anti-HLA sierici specifici del donatore rilevabili con un valore di intensità di fluorescenza media (MFI) di 500 al momento della biopsia o in qualsiasi momento prima.
Estrazione di RNA da campioni bioptici per la profilazione di mRNA e miRNAA ciascuno sono stati prelevati nuclei a due aghirenebiopsia dell'allotrapianto. Uno è stato utilizzato per la classificazione istologica convenzionale e almeno metà dell'altro è stato immediatamente conservato in Allprotect Tissue Reagent (Qiagen Benelux BV, Venlo, Paesi Bassi). Le provette Allprotect sono state conservate a 4°C (da un minimo di 24 a un massimo di 72 ore) , e quindi conservati a -20 gradi fino all'estrazione dell'RNA. L'RNA totale è stato isolato dalrenecampioni bioptici allotrapianti utilizzando il kit universale Allprep DNA/RNA/miRNA (Qiagen Benelux BV) su uno strumento QIAcube (Qiagen Benelux BV). La quantità (assorbanza a 26{{20}} nm) e la purezza (rapporto dell'assorbanza a 230.260 e 280 nm) dell'RNA isolato sono state misurate utilizzando lo spettrofotometro NanoDrop ND-1000 (Thermo Fisher Scientific/Life Technologies Europe BV, Gent, Belgio). Il numero di integrità dell'RNA (RIN) è stato valutato con il kit Eukaryote nano/pico RNA (Agilent Technologies Belgium NV, Diegem, Belgium) sullo strumento Bioanalyzer 2100 (Agilent Technologies Belgium NV). Gli indici di controllo di qualità non erano significativamente differenti tra VMI e No Gruppi MVI [RIN(media±DS):5.6±1.96vs5.4±1.97,P=0.66; rapporto 260/280 (media±DS):1.87±0.06 vs 1.87±0.1l,P{{26 }}.40]. Per campioni di RNA con un RIN basso(<6.5), we="" excluded="" samples="" with="" a="" 260/280=""><1.6. the="" extracted="" rna="" was="" subsequently="" split="" and="" stored="" at="" -80℃℃.half="" of="" the="" rna="" extract="" was="" used="" for="" mirna="" profiling="" and="" the="" other="" half="" for="" mrna="" transcriptomic="" analysis.="" the="" associated="" data="" are="" available="" from="" the="" gene="" expression="">

CISTANCHE MIGLIORERA' LA DIALISI RENALE/RENALE
Profilazione miRNASpecific reverse transcription of 150ngof total RNA was performed using Megaplex"RT Primers Human Pool A v2.1(Step 1)or Custom RT Primers Human Pool (Step 2 and 3)(Thermo Fisher Scientific, Les Ulis, France), on a Veriti Thermal Cycler (Applied Biosystems, Thermo Fisher Scientific). No complementary(c)DNA preamplification was required. miRNA expression was assessed by qPCR, using TaqManArray Cards (Applied Biosystems", Thermo Fisher Scientific), where the primers and probe of each miRNA were spottedanddried in duplicate wells of a microfluidic card. We used TaqMan"Array Human MicroRNA A +B Card Sets v3.0 for the discovery cohort(a two-card set enabling quantitation of 754 unselected human miRNAs)and Custom TaqManArray MicroRNA Cards for the selection and validation cohorts. Data analysis was performed by using Expression Suite software version 1.0.3. Assays with a cycle threshold(CT) values >35 sono state ritenute non espresse. RNU44 e RNU48 hanno mostrato un'espressione coerente in tutti i campioni, il coefficiente di variazione medio (RNU44 più RNU48) era del 3,73% nella scheda array A e del 3,79% nella scheda array B] e sono stati utilizzati come geni di pulizia per la normalizzazione dei dati in tutti i sottostudi.
Analisi trascrittomica dell'mRNAL'analisi trascrittomica è stata eseguita mediante microarray come già descritto(17). In breve, l'RNA totale estratto dai campioni bioptici è stato prima amplificato e biotinilato in RNA complementare (cRNA) utilizzando il GeneChip 39 IVT PLUS Reagent Kit (Affymetrix) e ibridato con Affymetrix GeneChip Human Genome U133 Plus 2.0 Array( Affymetrix), che comprendeva 54.675 set di sonde che coprivano l'intero genoma. Abbiamo utilizzato una normalizzazione della media robusta multichip (RMA). L'espressione normalizzata mediana di ciascun mRNA è stata confrontata tra casi e controlli utilizzando il test di Wilcoxon. Abbiamo controllato l'inflazione dell'alfa di rischio dovuta a test multipli applicando il metodo del tasso di false scoperte (FDR) di Benjamini & Hochberg. I dati del microarray sono stati gestiti in conformità con le linee guida dell'esperimento sulle informazioni minime sui microarray.
Analisi in silicoIl software Biological Interpretation Of Multiomics EXperiments (BIOMEX) è stato utilizzato per l'analisi differenziale dei dati trascrittomici, utilizzando l'annotazione ID Ensembl(18). Ingenuity Pathway Analysis (IPA, Build: 478438M Content version:44691306, Qiagen) e OMICSnet(19) sono stati utilizzati per determinare gli insiemi di geni regolati dai miRNA selezionati. OMICSnet è stato utilizzato per eseguire l'analisi dell'ontologia genica con il database del percorso Reactome, utilizzando il percorso completo (20). La costruzione di reti geniche è stata completamente senza supervisione e si è basata sul numero di interazioni molecolari riportate di ogni singolo gene con tutti gli altri geni nella rete. I geni che presentavano il maggior numero di interazioni sono stati automaticamente posizionati al centro della rete, mentre i geni con un numero inferiore di interazioni sono stati diffusi nella periferia. L'origine cellulare di miRNA selezionati è stata studiata utilizzando il progetto Fantom5(21), che fornisce un'analisi cap dell'espressione genica in cellule e tessuti umani. Per l'analisi dell'espressione di miRNA, abbiamo considerato tuttorene-cellule strutturali correlate e tutte le cellule ematopoietiche circolanti, senza ulteriore selezione.
Analisi dei dati di sequenziamento dell'RNA a cella singolaSono stati utilizzati dati di sequenziamento dell'RNA unicellulare umano precedentemente pubblicati (siRNA-seq) da due biopsie ABMR e quattro riferimenti sani corrispondenti a biopsie di sorveglianza del trapianto. I conteggi grezzi o le matrici associati sono stati scaricati rispettivamente da GEO(GSE145927, https://www.ncbi.nlm. nihgov/geo)(22) eReneProgetto di medicina di precisione (KPMP, https://atlas.kpmp.org/repository). Le matrici di espressione genica grezza generate per campione sono state unite e analizzate utilizzando il pacchetto Seurat V4 (23). I parametri applicati per creare e filtrare gli oggetti Seurat erano i seguenti: inclusione di cellule che esprimono tra 500 e 10000 geni rilevati e meno del 25% di trascrizioni mitocondriali. Dopo il filtraggio, tutti gli oggetti sono stati integrati utilizzando il flusso di lavoro di integrazione SCTransform su Seurat (24). In breve, sono state utilizzate 3000 funzionalità per l'integrazione utilizzando la funzione PrepSCTIntegration e la funzione FindIntegrationAnchors è stata utilizzata per limitare l'effetto batch. Un set di dati UMAP (Uniform Manifold Approssimation and Projection) completo è stato generato utilizzando la funzione DimPlot e i primi 16 componenti principali. I cluster sono stati creati utilizzando le funzioni FindNeighbors e FindClusters con una risoluzione di 0,6. L'identificazione del cluster è stata eseguita utilizzando la funzione FeaturePlot valutando l'espressione di marcatori specifici in ciascun cluster. I dot plot sono stati generati utilizzando le funzioni di tracciatura DotPlot e FeaturePlot, con conteggi normalizzati nel dosaggio dell'RNA come dati di input.

CISTANCHE MIGLIORERA' L'INFEZIONE RENALE/RENALE
Analisi statisticaLe caratteristiche del paziente e del donatore sono state descritte da numeri, percentuali e frequenze per variabili categoriali. Abbiamo riportato variabili continue utilizzando medie e deviazioni standard (SD) se normalmente distribuite, mediane e intervalli interquartile (IQR) per variabili con distribuzione asimmetrica. Abbiamo confrontato le loro caratteristiche utilizzando il test di Fisher o Wilcoxon quando appropriato. Abbiamo utilizzato il test di Kruskal-Wallis per confrontare l'espressione mediana del miRNA in base all'intensità dell'MVI e il test di Spearman per l'analisi di correlazione. Abbiamo considerato la significatività statistica per i valori P inferiori a 0.05. Abbiamo utilizzato GraphPad Prism (versione 8; GraphPad Software, San Diego, CA) e RStudio (versione 4.0.3) per l'analisi statistica e la presentazione dei dati. Sono stati utilizzati i seguenti pacchetti R: heatmap3 (heatmap3_1.1.9)per analisi heatmap, fmsb(fmsb_0.7.0)e scales (scales_1.1.1)pacchetti per grafici radar, ggplot2 (ggplot2_3.3.5)per i grafici a barre e complot(corrplot_0.90)per l'analisi della matrice di correlazione.
RISULTATI
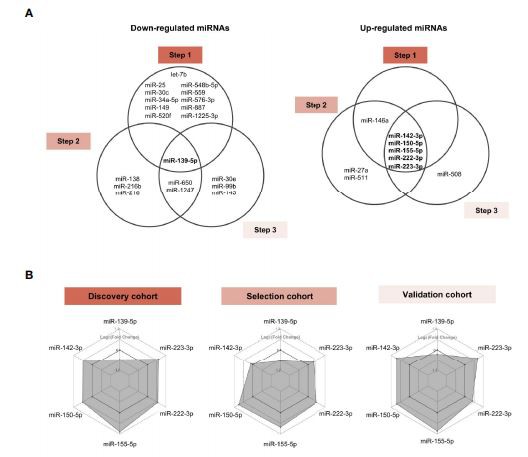
Identificazione multifase di miRNA associati a MVIBetween April 2013 and July 2015,646 patients enrolled in the BIOMARGIN study provided 716 indication or surveillance biopsies. Inadequate biopsies (N=49), biopsies with no paired sample for research use(N=135)or samples not passing molecular biology QC(N=49) were excluded, leaving 483 samples from 441 individuals available for this study (Figure 1A). Baseline and clinical characteristics of the study groups are provided in Supplementary Tables S1-3, and the histological characteristics of the biopsies are provided in Supplementary Tables S4-6. In the discovery cohort, a total of 27 patients met the MVI composite endpoint(MVI+), defined as clinical ABMR diagnosis and/or any level of MVI(g and/or ptc>0). Gli altri 59 pazienti (MVI-) hanno presentato varie diagnosi comprendenti rigetto mediato dai linfociti T (TCMR, N=8), fibrosi interstiziale e atrofia tubulare (IFIA, N=20) e biopsie normali (N{{6} }}), ma senza MVI. Dai 754 candidati miRNA, 18 miRNA sono stati espressi in modo differenziale tra i gruppi MVI plus e MVI- (Figura 1B). Nella coorte di selezione, un elenco ristretto di 143 miRNA è stato quantificato in 99 campioni. In questa coorte di selezione, 14 miRNA sono stati espressi in modo differenziale tra i casi con (N=28) e senza (N=71)ABMR (Figura 1C). Infine, nella più grande coorte trans-sezionale, 38 miRNA sono stati quantificati in 298 campioni, di cui 12 miRNA sono stati espressi in modo differenziale tra biopsie ABMR(N=29) vs no ABMR (N{22}}) (Figura 1D ).
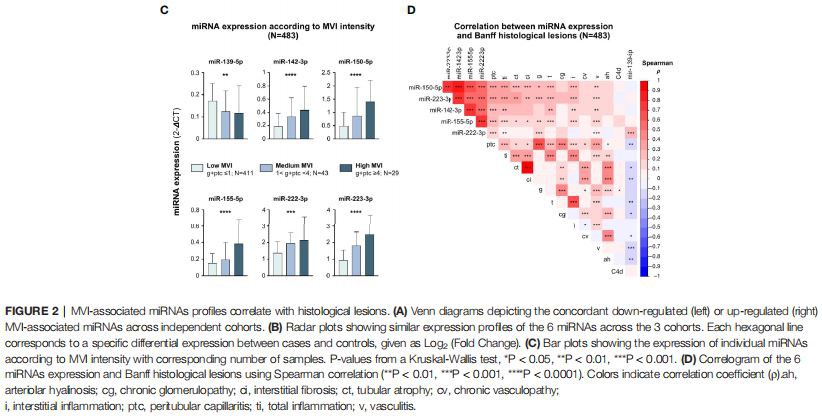
Identificazione coerente di 6 MiRNA associati a MVI e correlazione con l'istologiaSuccessivamente, abbiamo intersecato i 3 elenchi di miRNA differenzialmente espressi e identificato 6 miRNA che erano costantemente associati a MVI o ABMR nelle 3 coorti indipendenti (Figura 2A).miR-142-3p,miR-150-5p,miR -155-5p, miR-222-3p e miR-223-3p sono stati sovraespressi in MVI/ABMR, mentre l'espressione miR-139-5p è stata ridotta. I grafici radar (Figura 2B) mostrano per ogni passaggio l'espressione differenziale tra caso e controlli dei 6 miRNA e supportano la robustezza dei profili miRNA attraverso le tre coorti indipendenti. Successivamente, abbiamo studiato come l'espressione di 6 miRNA è associata a singole lesioni istologiche in tutte le 483 biopsie di allotrapianto presi insieme. L'espressione dei 5 miRNA up-regolati aumentava gradualmente con l'intensità delle lesioni MVI, mentre l'espressione di miR-139-5p era correlata negativamente (Figura 2C).MiR-139-5p/142-3p/ 150-5p/155-5p/223-3p non erano solo altamente associati alle caratteristiche correlate all'ABMR (g, ptc, deposizione di C4d), ma anche alle lesioni correlate alla TCMR (i, t ) e lesioni IFTA (ct, ci), suggerendo il loro coinvolgimento in processi infiammatori e cicatriziali comuni, non specifici per ABMR. In alternativa, potrebbe esistere per natura una collinearità intrinseca tra le lesioni, con conseguente incapacità di identificare la vera specificità per una lesione. MiR-222-3p non era correlato alle lesioni istologiche di TCMR o IFTA (Figura 2D).
Integrazione multi-omica: interazione mRNA-miRNA in MVSuccessivamente, abbiamo valutato i geni differenzialmente espressi tra i casi MVI plus e MVI-, nel discovery set precedentemente pubblicato (25). Delle 54.675 sonde, sono stati identificati un totale di 2755 geni differenzialmente espressi (DEG) tra MVI plus e MVI-
gruppi, comprendenti 1085 geni down-regolati e 1670 up-regolati (Figura 3A). Gli mRNA più espressi in modo differenziato nei campioni MVI plus erano CXCL9 e CXCL10, in linea con i precedenti rapporti (17,26) secondo cui questi geni sono i più sovraespressi nell'ABMR. Successivamente, abbiamo utilizzato IPA e OMICSnet per identificare in silico i presunti geni bersaglio per ciascun miRNA. Si prevedeva che un totale di 4504 mRNA sarebbero stati presi di mira da almeno uno dei 6 miRNA. Quindi, abbiamo integrato questi 4504 obiettivi previsti con i DEG nelle biopsie di allotrapianto. L'analisi integrata di miRNA/mRNA ha identificato 61 DEG presi di mira da miR-139-5p che erano significativamente aumentati in MVI più biopsie. Ha inoltre identificato 28, 58,52,43 e 27 DEG significativamente diminuiti in MVI più biopsie che erano rispettivamente bersaglio di miR-142-3p, miR-150-5p, miR-155-5p, miR{ {22}}p e miR-223-3p (Figura 3B).

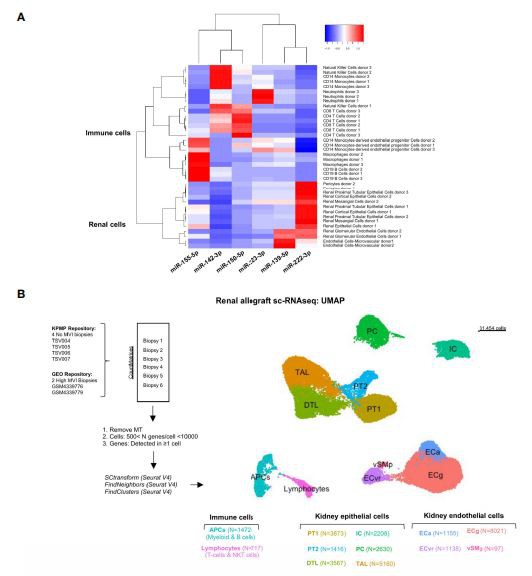
Origine cellulare dei miRNA associati a MVL'origine cellulare dei sei miRNA è stata caratterizzata in varirenalesottotipi cellulari ed ematopoietici utilizzando l'atlante di miRNA disponibili online [database Fantom (27)]. Il clustering non supervisionato è stato discriminatorenalemiRNA derivati dalle cellule da miRNA derivati dalle cellule immunitarie (Figura 4A). Ha anche rivelato uno o due tipi di cellule dominanti per ciascun miRNA. MiR-139-5p sembrava essere espresso principalmente dalle cellule endoteliali glomerulari (EC). MiR-222-3p, sebbene la sua espressione non fosse correlata all'infiammazione tubulare (lesioni di Banff"t", Figura 2D), era principalmente correlata arenalecellule epiteliali. I quattro miRNA rimanenti erano espressi principalmente nelle cellule mononucleate del sangue periferico (PBMC) o nei granulociti, con miR-142-3p arricchito in cellule NK e monociti, miR-150-5p in cellule T CD4 plus e CD8 plus, miR -155-5p in CD19 più cellule B e macrofagi e miR-223-3p in neutrofili.
Il sequenziamento dell'RNA a cellula singola ha identificato tutte le cellule renali e le cellule immunitarie infiltranti Per caratterizzare il potenziale ruolo di ciascun miRNA associato a MVI, abbiamo analizzato i dati sc-RNAseq disponibili pubblicamente da duerenalebiopsie di allotrapianto con ABMR e punteggi MVI elevati (g2, ptc3)(22). Questi set di dati sono stati integrati con 4 biopsie di riferimento sane senza MVI. Dopo il controllo di qualità e il filtraggio, sono state rilevate 31545 cellule e il clustering senza supervisione ha rivelato 12 cluster (Figura 4B). Abbiamo utilizzato marcatori consolidati(28) per identificare tutti i principali sottotipi di cellule residenti e infiltranti ed etichettarli (Figura supplementare S2). Successivamente, ci siamo concentrati sulle popolazioni cellulari da cui si pensava provenissero i nostri sei miRNA. A questo scopo, abbiamo stratificato le cellule in 4 cluster principali corrispondenti a endotelio, epitelio, linfociti e APC (Figura 4C). In linea con la precedente analisi di questi dati (22), nei dataset sc-RNASeg non sono state rilevate né popolazioni di cellule neutrofile né NK.
miR-139-5p Controlla l'attivazione dell'EC e il percorso di presentazione dell'antigene durante l'MVIMiR-139-5p è stato l'unico miRNA sottoregolato nel nostro studio nei casi con MVI/ABMR (Figura 2A) ed è stato riscontrato che proveniva principalmente dall'EC glomerulare (Figura 4A). Sessantuno dei suoi geni bersaglio è stato confermato essere sovraregolato in microarray di massa da casi MVI plus (Figura 3B) e la loro espressione è stata ulteriormente studiata alla risoluzione unicellulare nei 3 sottocluster EC precedentemente identificati (Figure 4B, C). Come illustrato nella Figura 5A, l'ECcluster attivato era rilevabile solo nei campioni MVI plus. Inoltre, la metà dei 61 geni (N=30) è stata costantemente aumentata in sc-RNAseq MVI più biopsie, indipendentemente dai tre sottocluster EC. Tra questi, GBP5 era il gene più aumentato. Successivamente, l'analisi dell'ontologia genica utilizzando queste 30 trascrizioni di derivazione endoteliale ha identificato UBE2D1 e YWHAG come attori centrali nella rete genica (Figura 5B). Più specificamente, sono stati arricchiti i percorsi immuno-correlati e i percorsi di elaborazione e presentazione dell'antigene mediati dal complesso di istocompatibilità maggiore (MHC) (Figura 5C). L'analisi pseudotemporale è stata eseguita per caratterizzare meglio i cambiamenti dell'espressione genica nel corso dell'attivazione della CE, la traiettoria dello stato attraverso le cellule (Figure 5D, E), UBE2D1, YWHAG e GBP5 sono aumentati continuamente durante l'attivazione endoteliale associata a MVI. Sono state trovate traiettorie molto simili per i geni correlati all'MHC HLA-A,-B e -DRA, ma anche per l'attivazione endoteliale in buona fede e i marcatori di infiammazione come VCAM1, CXCL9 e CXCL10, suggerendo che tutti questi geni sono espressi contemporaneamente durante l'attivazione endoteliale. Complessivamente, questi risultati suggeriscono che miR-139-5p è diminuito durante le lesioni MV e non reprime più il percorso di presentazione dell'antigene MHC nell'EC attivata.

miR-222-3p danneggia entrambiRenalePercorsi fisiologici e immuno-correlati nelle cellule epiteliali durante MVI Successivamente, ci siamo concentrati su miR-222-3p, un miRNA sovraregolato nei campioni MVI con unrenaleorigine delle cellule epiteliali e una correlazione più esclusiva con le lesioni istologiche correlate all'ABMR (Figure 2A, D, 4A). Nel tessuto allotrapianto sfuso, l'espressione di 43 dei suoi geni bersaglio è stata sottoregolata (Figura 3B) e ulteriormente valutata in un singolo- risoluzione cellulare nel diversorenalepopolazioni epiteliali precedentemente identificate (Figure 4B, C). Una massiccia diminuzione di 41 di questi 43 (95%) geni in tutti identificatirenalecluster di cellule epiteliali suggeriscono un silenziamento genico


profilo in VMI (Figura 6A). È interessante notare che 4 geni coinvolti inrenalepercorsi fisiologici (ERBB4, ATPIB1, TIMM50 e KIF3B), ma anche geni immuno-correlati (TRAPI e PEBPI) sono stati identificati come geni centrali nella rete (Figura 6B). L'ontologia genica dei geni 43 ha rivelato l'arricchimento nelle vie di segnalazione di ErbB ma anche nelle vie immuno-correlate e la risposta alle citochine (Figura 6C) e l'espressione di ERBB4 sono state ulteriormente confermate in tuttorenalecellule (Figura 6D). Complessivamente, questi risultati suggeriscono che durante VMI, un livello elevato di-222-3p inrenalecellule epiteliali è associata a una forte repressione dei geni coinvolti in entrambirenalevie dell'omeostasi degli elettroliti e vie immuno-correlate nell'epitelio.

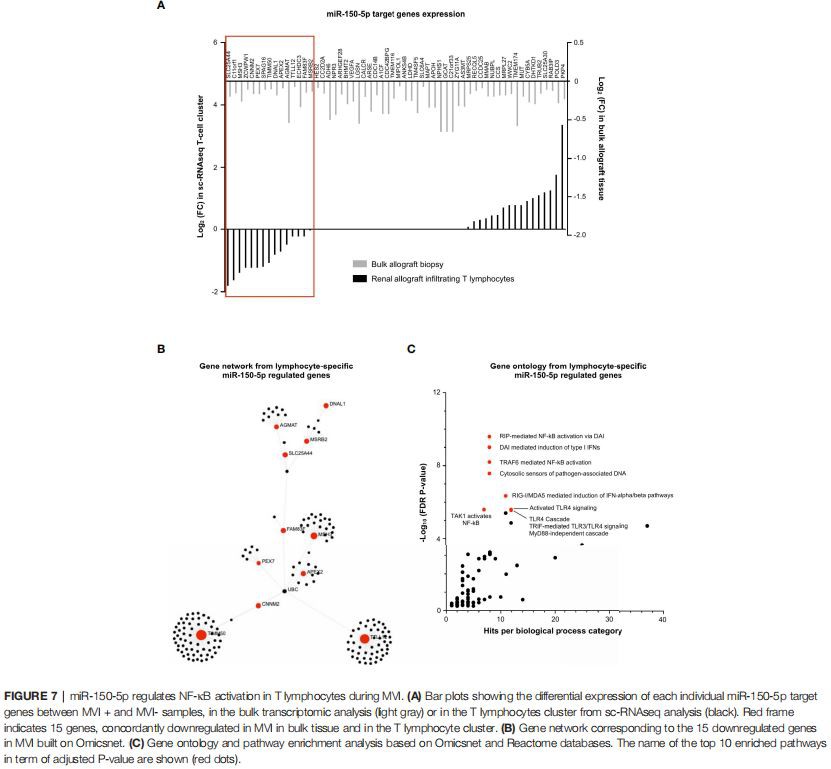
miR-150-5p regola l'attivazione di NF-kB nei linfociti T durante MVI Allo stesso modo, abbiamo studiato il ruolo regolatorio di miR (aumentato)-150-5p durante MVI nel cluster di cellule T, in cui era espresso in modo più dominante (Figura 4A). Abbiamo tracciato i 58 DEG associati a MVI diminuiti identificati nei campioni di biopsia di allotrapianto di massa (Figura 3B) e l'abbiamo confrontato con l'espressione genica nel cluster di cellule T sc-RNAseq (Figura 7A). La proporzione di geni entrambi presi di mira da miR150-5p e specificamente sottoespressi nei linfociti T durante MVI era sorprendentemente bassa (15/58,25,9 percento) suggerendo che la diminuzione globale di questi geni in vivo non era esclusivamente dovuta al Compartimento dei linfociti T. Tuttavia, da questo elenco altamente selezionato di 15 geni e utilizzando la piattaforma OMICSnet, abbiamo costruito una rete genica (Figura 7B) ed eseguito l'analisi dell'ontologia genica (Figura 7C). Abbiamo osservato che la sovraespressione di miR-150-5p era associata a NF -Regolazione KB nei linfociti T durante MVI.
miR-155-5p Regola lo splicing dell'mRNA negli APC durante MV Infine, la stessa identica strategia è stata applicata per i geni bersaglio 52miR-155-5p, sottoespressi durante MVI (Figura 3B). In contrasto con miR-150-5p nei linfociti T, abbiamo osservato che quasi i due terzi dei geni mirati a miR-155-5p sono stati costantemente ridotti nel cluster APC sc-RNAseq (31/52,59,6 percento, Figura 8A). L'analisi della rete genica ha rivelato che AIFMI e CIAO1 erano geni centrali (Figura 8B). Inoltre, l'ontologia genica ha rivelato un forte arricchimento nei percorsi relativi allo splicing dell'mRNA (Figura 8C).
DISCUSSIONEGrazie al suo design unico, lo studio BIOMARGIN è la struttura tipica per l'integrazione di dati multi-omici. In effetti, sono state utilizzate pipeline molto solide sia in coorti di scoperta, selezione e validazione che comprendevano un gran numero di pazienti provenienti da diversi centri di trapianto. Nelle tre coorti indipendenti, abbiamo contemporaneamente osservato e confermato il peculiare profilo di espressione di 6 miRNA durante MVI: miR-139-5p era diminuito mentre miR-142-3p/150-5p/{{5} }p/222-3p e miR-223-3p sono stati aumentati. È importante sottolineare che il livello di ciascuno di questi 6 miRNA era correlato alla gravità dell'MVI, suggerendo un meccanismo di regolazione dose-dipendente. Successivamente abbiamo utilizzato in piattaforme di silicio per studiare ogni origine cellulare di miRNA. Sorprendentemente, sono stati osservati due gruppi distinti di miRNA: un primo derivato da cellule immunitarie infiltranti e un secondo più specifico per residentirenalecellule. Quindi, sia i miRNA che gli mRNA sono stati misurati nello stesso set di scoperte di campioni bioptici, consentendo un'analisi integrata di mRNA/miRNA differenzialmente espressi in vivo e convalidati associati a MVI. Infine, dopo aver descritto l'associazione mRNA/miRNA alla risoluzione del tessuto di massa, abbiamo confermato l'interazione tra mRNA/miRNA alla risoluzione unicellulare per quattro dei 6 miRNA identificati.
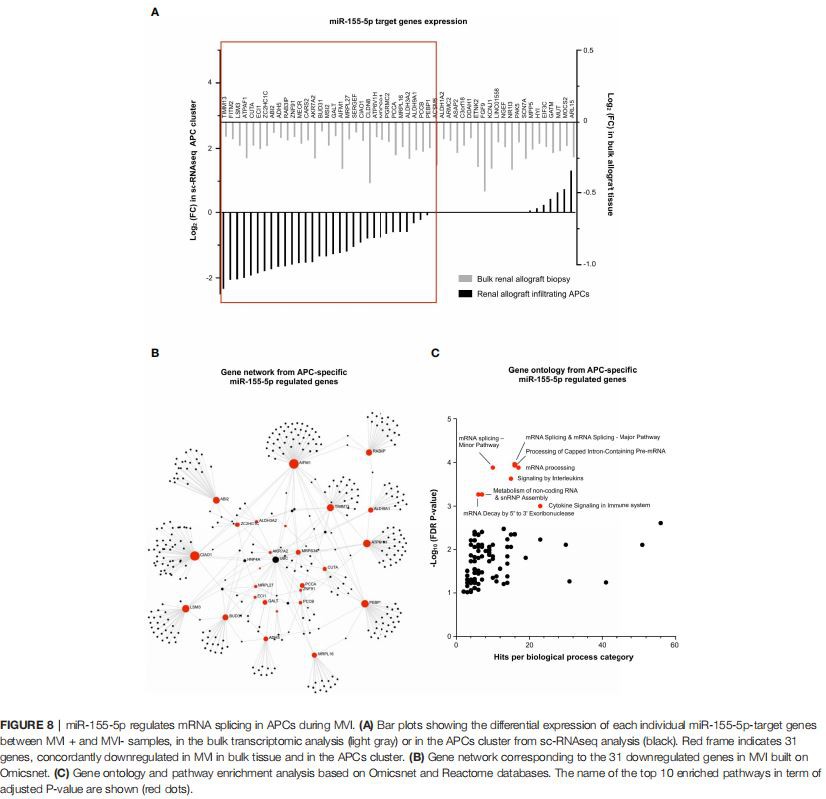
È interessante notare che miR-139-5p era l'unico miRNA correlato negativamente con le lesioni MVI. Ha avuto origine principalmente dalla CE ed è stato segnalato per regolare i geni correlati all'MHC. Tra i suoi geni bersaglio, UBE2D1 era altamente sovraregolato durante l'attivazione endoteliale associata a MVI. La famiglia UBE2D è una famiglia di enzimi di coniugazione dell'ubiquitina E2 nel sistema ubiquitina-proteasoma (29, 30) e UBeD1 ha dimostrato di migliorare l'ubiquitinazione di marzo I, portando all'up-regulation delle proteine MHC di classe II (31). Inoltre, GBP5 era il gene inattivato EC più rappresentato durante MVI, il che è in linea con i nostri recenti rapporti che mostrano che GBP5 è altamente sovraregolato nelle biopsie ABMR(17) ma anche nei campioni di sangue(32). È interessante notare che l'espressione di GBP5 ha dimostrato di essere inducibile dall'interferone di tipo II nelle cellule endoteliali microvascolari uterine umane, insieme a CXCL9 e CXCL10(33). Il ruolo precoce di queste due chemochine proinfiammatorie nei processi di rigetto acuto è ben documentato e il loro livello nelle urine è proposto per monitorare il rischio di rigetto acuto nella sorveglianza di routine dei pazienti sottoposti a trapianto di rene (34). Un altro target miR-139-5p è il codice YWHAG.YWHAG per la famiglia proteica di HLA-F ed è stato descritto come espresso in modo differenziale durante il processo profibrotico attivo nella nefropatia diabetica (35). Il possibile ruolo di miR-139-5p nella fibrosi, un percorso comune finale dopo l'infiammazione, è tanto più rilevante che l'IFTA è stato recentemente incluso in un punteggio composito per predire la sopravvivenza dell'allotrapianto renale dopo ABMR(36). Complessivamente, questi risultati suggeriscono che miR-139-5p non reprime più l'espressione dell'antigene MCH sulla superficie dell'aneto durante MVI e potrebbe partecipare al processo di chemioattrazione e fibrosi, ma questi meccanismi devono essere confermati sperimentalmente espressione sulla superficie dell'endotelio durante MVI e potrebbero partecipare ai processi di chemioattrazione e fibrosi, ma questi meccanismi devono essere confermati sperimentalmente.
Il secondorenale-il miRNA derivato che abbiamo identificato è miR-222- 3p, la cui espressione è risultata essere più specifica delle lesioni MVI: è associato ai punteggi g e PTC nonché alla deposizione di C4d, ma non alle lesioni i o t. Tuttavia, proveniva principalmente dalle cellule epiteliali. Dopo l'integrazione multi-omica alla risoluzione cellulare, abbiamo determinato che miR-222-3p reprime principalmente la segnalazione di ErbB che è cruciale per le funzioni cellulari fondamentali, come la proliferazione, la migrazione, la crescita e il differenziamento (37). Nella biologia umana, è necessaria la segnalazione fisiologica di ErbBrenaleomeostasi elettrolitica e mantenimento dell'integrità renale (38). I nostri risultati hanno anche identificato ADAM22, NRG1, ZNF91 come geni correlati alla segnalazione di ErbB, in particolare repressi nell'epitelio durante MVI. Anche altri geni essenziali per la fisiologia renale come ATP1B1 e KIF3B sono stati repressi nell'epitelio renale da miR-222-3p durante MVI. In precedenza, Baker et al. ha mostrato che ATP1B1 (subunità b1 di Na più /K più -ATPasi) guidarenaleriassorbimento tubulare del sodio (39). Inoltre, Aguado-Fraile et al. hanno identificato il membro della famiglia Kinesin 3B (KIF3B) come coinvolto nel traffico cellulare nelle cellule del tubulo prossimale di ratto. KIF3B appare come un mediatore chiave della risposta delle cellule del tubulo epiteliale prossimale all'ischemia/riperfusione con potenziale applicazione inrenalegestione del danno ischemico (40). Possiamo quindi ipotizzare che miR-222-3p reprimi i percorsi fisiologici essenziali durante MVI nell'epitelio. Inoltre, le vie immunitarie sono regolate anche dalla sovraespressione di miR-222-3p: geni importanti come TRAP1 e PEBP1 sono stati totalmente inibiti in campioni con MVI forte. È interessante notare che TRAP1 ha dimostrato di migliorarerenalefibrosi tubulointerstiziale nei topi con ostruzione ureterale unilaterale mediante protezionerenalemitocondri delle cellule epiteliali tubulari (41). Inoltre, PEBP1 fornisce effetti antinfiammatori attraverso l'inibizione delle vie MAPK e NF-kB in condizioni omeostatiche/basali (42). Inrenaleepitelio, uno studio di Marko et al. ha mostrato elegantemente che l'attivazione post-ischemica di NF-kB aggrava il danno tubulare ed esacerba l'infiammazione (43). Nelle nostre mani, PEBP1 è stato completamente represso da miR-222-3p, suggerendo che il percorso NF kB si scatena durante MVI. Complessivamente, questi risultati mostrano che la biologia epiteliale è disturbata durante MVI erenalele cellule epiteliali rispondono attivamente alle lesioni MVI mentre il coinvolgimento di questo tessuto in MVI viene raramente affrontato. Questi risultati molecolari potrebbero gettare nuova luce sulle lesioni tubulari acute, un criterio ABMR consolidato, ma a lungo trascurato. Inoltre, è stato dimostrato che le cellule epiteliali possono secernere miR esosomale-222-3p e indurre il fenotipo M2 nei macrofagi (44). Nel frattempo Li et al. molto recentemente ha riportato che i macrofagi M2 sovraesprimono miR-155 e rilasciano questo miRNA nel microambiente, anche attraverso la secrezione di esosomi. Nel trapianto di rene, miR-155 è stato aumentato in varie condizioni (IFTA, rigetto acuto e TCMR) e nei fluidi corporei o nei tessuti (45). È interessante notare che miR- 155 può promuovere la transizione epiteliale-mesenchimale mirando a RASSF4 nelle cellule epiteliali (46). Questo crosstalk basato su miRNA tra macrofagi erenalecellule epiteliali devono ancora essere valutatetrapianto renalee più in particolare nel contesto di MVI. In linea con questi risultati, abbiamo osservato che miR-155-5p era espresso principalmente da APC che comprendevano monociti e macrofagi. In questo particolare sottoinsieme, l'ontologia dei geni p-target miR- 155-5 ha rivelato l'arricchimento nelle vie di splicing del premRNA. È interessante notare che Janssen et al. ha riferito che l'infiammazione polmonare ha indotto percorsi di splicing pre-mRNA nei macrofagi alveolari. Inoltre, l'attivazione dello splicing pre-mRNA differiva nei macrofagi residenti nei tessuti rispetto ai macrofagi derivati dai monociti (reclutati dal sangue). Sono stati riportati cambiamenti nel metabolismo centrale nei macrofagi reclutati, con aumento dell'efflusso attraverso la glicolisi e diminuzione dell'efflusso attraverso il ciclo dell'acido tricarbossilico (ciclo TCA, cioè ciclo di Krebs) (47). Per quanto riguarda miR-150-5p, abbiamo scoperto che la sua sovraespressione durante MVI era associata alla via NF-kB nel cluster di linfociti che comprendeva sia le cellule NKT innate che le cellule T adattative. È interessante notare che miR-150-5p è fondamentale per generare cellule NK mature e funzionali (48) e cellule T CD8 carenti di miR-150-5p sono risultate meno citotossiche (49). Inoltre, le cellule T CD8 possono anche secernere miR-150-5p negli esosomi (50) che a loro volta potrebbero promuovere l'attivazione dei fibroblasti nelle cellule epiteliali tubulari e la successivarenalefibrosi come suggerito da recenti studi (51, 52).

La cistanche migliorerà la funzionalità renale/renale
Il nostro studio ha alcuni limiti. Abbiamo concentrato la nostra ricerca su 6 miRNA, costantemente identificati nel nostro design multistep. Tuttavia, abbiamo proceduto con una selezione graduale dei miRNA, con solo una frazione di tutti i miRNA noti quantificati nella coorte di convalida. Il percorso statistico per la selezione dei miRNA si basava sul progetto iniziale di BIOMARGIN, adatto per identificare biomarcatori diagnostici per endpoint multipli (ABMR, ma anche TCMR e IFTA). Quindi, sebbene significativamente aumentato nelle coorti di scoperta e selezione (Figura 2A), miR-146a non è stato quantificato nella coorte di convalida. Pertanto, miR-146a è stato di fatto escluso dal nostro processo di selezione, sebbene la letteratura suggerisca un ruolo nell'ischemia/riperfusione nel trapianto di rene (53) e nel controllo mediato da Treg delle risposte alloimmuni (54). Inoltre, non possiamo escludere che una dimensione del campione più potente avrebbe prodotto più miRNA, come miR-138 (down) e miR-511 (up) che erano espressi in modo differenziale nei casi ABMR della coorte di selezione e ha mostrato una tendenza nella stessa direzione nella coorte di scoperta. Inoltre, non abbiamo eseguito l'analisi sc-RNAseq sui nostri campioni di biopsia, ma abbiamo utilizzato un set di dati sc-RNAseq disponibile online. Al momento della progettazione dello studio e della raccolta dei campioni bioptici, la tecnologia scRNAseq non era ancora disponibile e la necessità di campioni appena raccolti non consentiva l'uso retrospettivo di campioni congelati o inclusi in paraffina. Allo stesso modo, la profilazione dell'mRNA è stata eseguita utilizzando microarray, la tecnologia di riferimento all'epoca che ora è stata superata dall'RNA-seq di prossima generazione. L'uso di un set di dati sc-RNAseq disponibile online sta limitando la nostra capacità di riportare le caratteristiche demografiche di base dei pazienti. Questa informazione mancante potrebbe destare preoccupazione per quanto riguarda la rappresentatività dei gruppi di popolazione. Inoltre, non abbiamo controllato alcun aspetto tecnico del sequenziamento. Quindi, alla risoluzione scelta, la nostra analisi sc-RNAseq non ha rilevato alcun cluster di neutrofili o cellule NK in questi campioni. Pertanto, le nostre analisi a valle di miR-142-3p e miR-223-3p si sono limitate alla creazione della rispettiva rete e ontologia del gene target (Figura supplementare S2) e non hanno consentito alcuna esplorazione della risoluzione di una singola cellula. Tuttavia, la rete genica e l'ontologia dei 27 geni bersaglio di miR-223-3p hanno rivelato l'arricchimento del ciclo TCA (Figura supplementare S2) insieme alla segnalazione ERBB. Possiamo quindi ipotizzare che sia miR-155-5p nei monociti che miR-223-3p nei neutrofili svolgano un ruolo nel metabolismo e nella risposta infiammatoria impegnata da queste cellule durante MVI. Inoltre, è già stato dimostrato che miR-142-3p è aumentato nel rigetto dell'allotrapianto renale (9, 55, 56), ma finora non era stato specificamente associato all'ABMR. Un'altra limitazione del nostro studio è che i cambiamenti specifici dell'espressione genica nelle rare cellule infiltranti potrebbero essere mascherati nell'analisi dell'espressione genica di massa. Sono quindi necessari ulteriori studi che includono più campioni per consentire un'indagine adeguata di tutti, anche i sottotipi cellulari rari, ma sono attualmente limitati dal costo relativamente elevato della tecnica.
In conclusione, abbiamo studiato qui le vie molecolari associate all'MVI, il principale danno istologico correlato all'ABMR. L'approccio omico integrato utilizzato ci ha permesso di svelare nuovi percorsi coinvolti nell'MVI e suggerisce che le modificazioni del metabolismo epiteliale tubulare si verificano come conseguenza dell'ABMR, oltre il vicino compartimento endoteliale. Il nostro studio illustra il grande potenziale della multi-omica per svelare i meccanismi della malattia e apre la strada a nuove indagini per chiarire ulteriormente il cross-talk trarenalesottoinsiemi di cellule residenti e infiltranti l'allotrapianto.
